|
Ecco un metodo per valutare il funzionamento di un antibiotico:
con una pinza sterile si pone su piastra opportunamente trattata (con un terreno di coltura
per determinare la sensibilità agli antibiotici) una certa quantità di antibiotico;
questo si diffonde formando un alone; si misura il diametro dell'alone, detto diametro di inibizione.
Sappiamo che il diametro cresce grosso modo linearmente col logaritmo della concentrazione di antibiotico.
Rappresenta con una retta la relazione tra il logaritmo decimale LA della concentrazione di
antibiotico A (in una opprtuna unità di misura) e il diametro medio D di inibizione (in mm) di un germe sensibile all'antibiotico nel caso in cui per A pari a 1, 2, 5 e 10 si ottengano per D i valori 21.1, 23.5, 27.0, 30.1.
Valuta qual è il diametro di inibizione per la concentrazione 7. | | 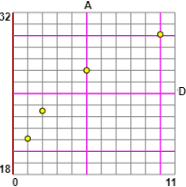 |
Trasformo di dati "A" applicando il logaritmo in base 10 (Log). Utilizzo questa
calcolatrice cliccando [Log]:
1, 2, 5, 10 → 0, 0.30102999566398114, 0.6989700043360187, 1
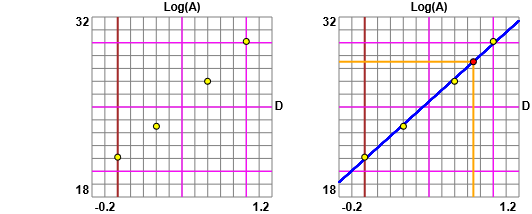
A sinistra la rappresentazione grafica di quanto ottenuto realizzata con questo script
(la figura iniziale è stata ottenuta con questo).
Si vede come i dati siano molto allineati.
Possiamo trovare la retta che li aspprossima con quest'altro
script.
x: 0, 0.30102999566398114, 0.6989700043360187, 1
y: 21.1, 23.5, 27.0, 30.1
y = 8.972015324170837 * x + 20.938992337914577
Sopra a destra la rappresentazione dei punti assieme alla retta
y = 8.972*x + 20.939, rappresentazione ottenuta con questo script. Dal grafico
posso ricavare il diametro di inibizione per la concentrazione 7: dato che Log(7) = 0.8450980400142567 trovo che all'ascissa 0.845
corrsiponde l'ordinata 28.5 (vedi il punto rosso). Volendo posso calcolare 8.972*0.845 + 20.939 = 28.52034, che comunque devo arrotondare
con meno cifre.
Vediamo come usare R (vedi):
source("http://macosa.dima.unige.it/r.R") # se non lo hai gia' caricato
D = c(21.1,23.5,27.0,30.1)
A = c( 1, 2, 5, 10)
BF=3; HF=2.5
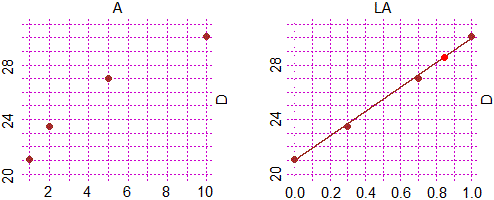
# Il grafico A,D
Plane(1,10, 20,31)
POINT(A, D, "brown"); abovex("A"); abovey("D")
# Il grafico LA,D
LA = log10(A); range(LA)
# 0 1
Plane(0,1, 20,31)
POINT(LA, D, "brown"); abovex("LA"); abovey("D")
# La retta di regressione
regression1(LA,D)
# 8.972 * x + 20.94
f = function(x) 8.972*x+20.94
# la verifica grafica
graph1(f, 0,1, "brown")
# Il punto cercato:
x=log10(7); x; f(x)
# 0.845098 28.52222
POINT(x,f(x), "red")
 # Il diametro di inibizione per la concentrazione 7 è 28.5 mm
# Il diametro di inibizione per la concentrazione 7 è 28.5 mm



